研究 (Research)
最終更新日:
膵がん組織の詳細な「単細胞地図」の完成と創薬応用 (Completion of a detailed “single cell map” of pancreatic cancer tissue and its application in drug discovery)
教授 江口 英利、特任教授(常勤) 石井 秀始 (医学系研究科) EGUCHI Hidetoshi, ISHII Hideshi (Graduate School of Medicine)
研究の概要
膵がんの予後は極めて不良であり、その克服には、早期段階や病態の変化を正確に診断する画期的な技術の開発と、その知見に基づいた創薬基盤の構築が必要です。私たちは、大阪大学医学部附属病院で膵がんの診療を受けた患者さんの試料から得た単一細胞 RNA シーケンシング(scRNAseq)のデータに、国内外で既に行われた scRNAseqのデータを加え、最大規模の膵がんに関する詳細な「単細胞地図」を完成させました。合計で70以上のサンプル、13万以上の細胞を含むデータセットから膵管腺癌(PDAC)の単一細胞アトラスを構築し、従来のトランスクリプトーム情報の統合的解析に加え、細胞間コミュニケーションの詳細な検討を行いました。
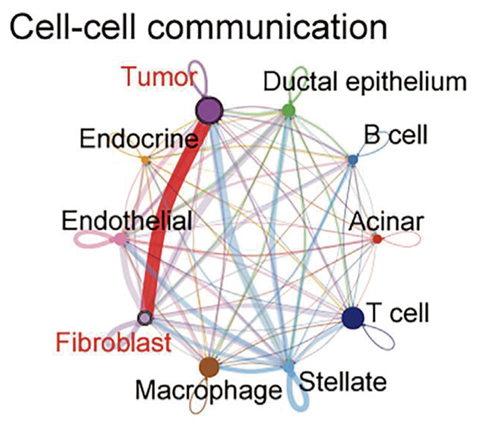
この解析により、膵がんの多様性を構成する一つ一つの細胞の情報を解明し、画期的な創薬のための基盤情報を構築しました。解析結果は、膵がん細胞が微小環境ニッチにおいて、線維芽細胞サブタイプに応じた生存戦略を取ることを明らかにし、新たな治療標的の可能性を提示しました。
研究の背景と結果
膵管腺癌(PDAC)は膵臓の管状上皮細胞から発生し、非常に限られた治療法と極めて低い生存率を特徴とする致命的な疾患です。5年生存率はわずか9% に過ぎず、予後が悪い主な要因として、早期発見が困難であることや、早期に転移が発生するため、手術による完全切除が困難なケースが多い点が挙げられます。PDAC の進行過程では、KRAS、TP53、SMAD4、CDKN2A といった主要な遺伝子変異が蓄積されますが、これらの変異に対する効果的な標的治療は依然として確立されていません。
また、腫瘍微小環境(TME)は血管、免疫細胞、線維芽細胞など多様な細胞群で構成されており、腫瘍の不均一性や悪性 度 に 大 き く 影 響 を 与 え ま す。最 近 の シ ン グ ル セ ル 転 写 解 析(scRNAseq)は、TME の理解を深め、細胞状態や相互作用に関する重要な知見をえることができました。これにより、新たな腫瘍サブタイプや細胞間の相互作用が特定され、PDAC の生物学に関するより精密な研究が進展しています。これまでに、130,000以上の細胞を含むscRNAseq データセットを用いて PDAC を細胞レベルで分析し、さらに TCGA の RNAseq データを再解析することで、腫瘍と癌関連線維芽細胞(CAF)の間のコミュニケーションを明らかにしました。公開されているリファレンス単細胞トランスクリプトームのデータセットは、異なる研究グループにより報告されていますが、臨床環境やサンプリング方法、使用する scRNAseq プラットフォームの違いにより、一貫性 に 欠 け て い ま す。
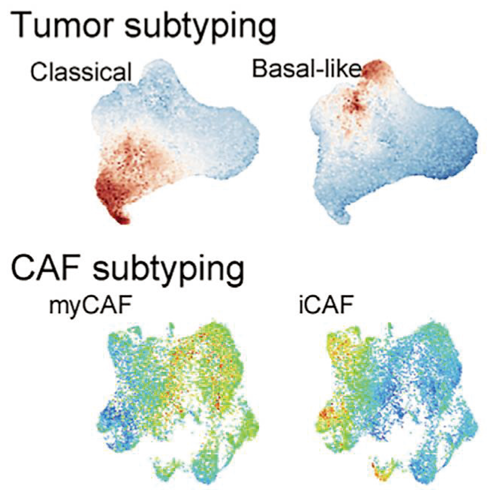
そ こ で 我 々 は、5 つ の 公 開 デー タ セッ ト( PRJCA001063、 GSE111672、 GSE154778、 GSE155698、GSM4293555)と我々のデータ(OUGS)を統合し、バッチ補正を行ってリファレンスツールを構築しました。これにより、差次的遺伝子発現を用いて、正常および悪性の上皮細胞を含む10種類の細胞タイプを特定しました。患者間の細胞比率に違いはあるものの、データセット全体で一貫した傾向が見られ、統合は成功しました。
転写解析における遺伝子発現の統合と再解釈としては、統合データを UMAP で可視化し、細胞タイプとそのモジュールスコアを表示したところ、TCGA PAAD における遺伝子発現変化を引き起こす鍵となる細胞由来の遺伝子を特定しました。線維芽細胞、B 細胞、マクロファージは、間質組織の形成と免疫浸潤に寄与し、腺房細胞の機能喪失が顕著で、膵がんの病態を反映していました。
研究の意義と将来展望
本研究における詳細な「単細胞地図」の完成により、がん幹細胞の位置が明らかになり、がん微小環境のニッチの構成、さらには細胞間の情報伝達の内容も解明されました。これにより、精密医療の社会実装に向けた大きな一歩を踏み出すことができます。
担当研究者
教授 江口 英利、特任教授(常勤) 石井 秀始 (医学系研究科)
キーワード
膵がん/シングル細胞/がん微小環境
応用分野
医療・ヘルスケア、創薬
参考URL
https://resou.osaka-u.ac.jp/ja/research/2022/20220705_1
https://researchmap.jp/abcdabcdabcd
https://researchmap.jp/30452436
https://researchmap.jp/read0103186
